info@genecompany.com|
基因快讯|


技术交流

扫描二维码
或添加“GeneGroup003”
获取更多更新资讯
商城订购

扫描二维码
或添加“基因商城(GeneMart)”
手机下单,快人一步
售后服务

扫描二维码
或添加“GeneGroup005”
获取更快速售后支持
【NEB上新啦!】告别重亚硫酸盐——看ta如何用酶学转化法特异性检测5hmC位点!

继2019年重磅推出高效替代重亚硫酸盐的酶学转化法甲基化建库试剂盒EM-seq后,NEB再次推出全球独创性产品——
NEBNext® 酶学转化法 5hmC 甲基化建库试剂盒 (E5hmC-seq™)
这是一种在单碱基水平上特异性检测5hmC位点的新方法。
通常,使用基于NEBNext EM-seq酶学转化或重亚硫酸盐转化生成的Illumina文库,可以检测修饰的5-甲基胞嘧啶(5mC)和5-羟甲基胞嘧啶(5hmC)。然而,这些方法并不能区分5mC和5hmC。
与EM-seq相同,NEBNext®酶学转化法5hmC甲基化建库试剂盒(E5hmC-seq™)使用酶学转化法特异性检测5hmC位点,不会像重亚硫酸盐转化法对DNA造成损伤,即便DNA起始量低至0.1 ng,也能灵敏地检测5hmC位点。
用于EM-seq和重亚硫酸盐测序的生物信息学分析工具也可用于E5hmC-seq。可以从EM-seq数据中减去E5hmC-seq数据,从而确定单个5mC和5hmC的精确位置。
E5hmC-seq 转化原理

在两步酶法转化过程中,首先对5hmC进行糖基化,使得5hmC在下一步脱氨基反应中被保护了起来,而未被保护的5mC和未甲基化的胞嘧啶会被脱氨基为尿嘧啶。随后使用NEBNext®Q5U®预混液(Q5®高保真DNA聚合酶的改良版)进行扩增,并在Illumina平台上进行测序。
产品优势
1. 卓越的5hmC检测灵敏度 2. 起始量范围广:0.1–200 ng 3. 更均一的GC覆盖度 4. 更高效的建库流程 5. E5hmC-seq和EM-seq数据结果可联合分析 6. 可单独购买转化模块(NEB #E3365)
部分数据结果

使用Covaris® ME220仪器将0.1 ng至200 ng人脑基因组DNA打断至350 bp,并用E5hmC-seq的起始样本,所使用的PCR循环数如图所示。使用 Agilent®TapeStation®,High Sensitivity D1000试剂测定文库产量。显示的数值是四次技术性重复的平均值,误差线表示标准差。 结果表明:不同起始量的样本均能获得高产量的E5hmC-seq文库。
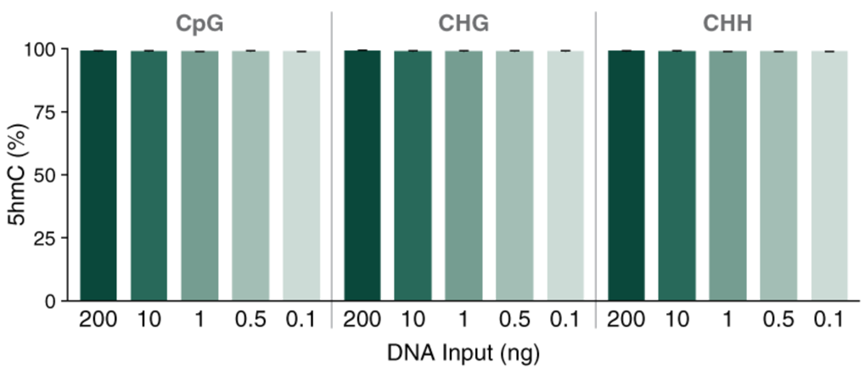
使用0.1 ng至200 ng人脑基因组DNA制备E5hmC-seq文库时,插入所有胞嘧啶完全羟甲基化的T4 DNA作为标准品。使用Covaris®ME220 仪器将DNA打断至 350 bp,并用作E5hmC-seq的起始样本,构建的文库在Illumina®NovaSeq 6000(2x150 bases)上进行测序。使用bwa-meth将每个文库的19亿数据(200 ng、10 ng和1 ng)或7.15亿数据(0.5 ng和0.1 ng)与人类T2T、lambda和T4参考基因组的复合基因组进行比对。使用MmethylDackel从比对结果中提取甲基化信息。显示的数值是两次技术性重复的平均值,误差线表示标准差。 结果表明:T4 DNA标准品CpG、CHG和CHH中的5hmC检出率≥ 98.9%。

使用Covaris® ME220 仪器将0.1 ng 至200 ng人脑基因组DNA打断至350 bp,并用作E5hmC-seq的起始样本,构建的文库在Illumina NovaSeq 6000(2x150 bases)上进行测序。使用bwa-meth将每个文库的19亿数据(200 ng、10 ng 和 1 ng)或7.15亿数据(0.5 ng 和0.1 ng)与人类T2T、lambda和T4参考基因组的复合基因组进行比对,并使用MmethylDackel从中提取甲基化信息。显示的数值是两次技术性重复的平均值,误差线表示标准差。 结果表明:不同起始量的样本在CpG、CHH 和CHG中的5hmC占比相似。
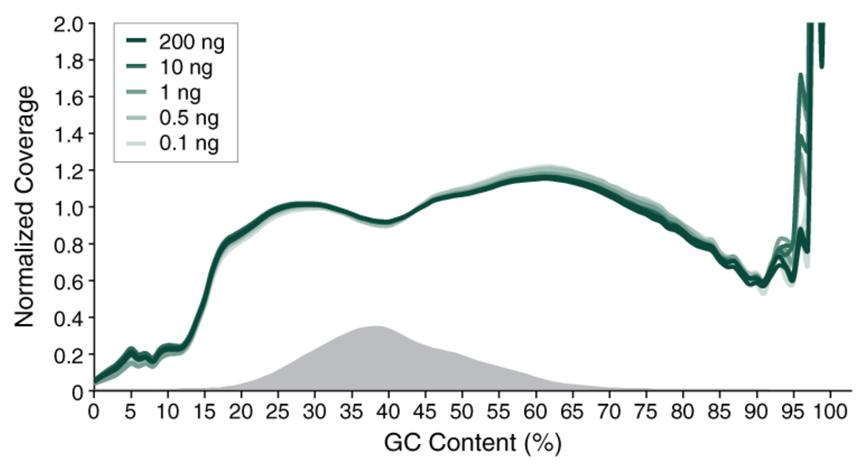
使用Covaris ME220 仪器将0.1 ng 至200 ng人脑基因组DNA打断至350 bp,并用作E5hmC-seq的起始样本,构建的文库在Illumina NovaSeq 6000(2x150 bases)上进行测序。使用bwa-meth 将每个文库的19亿数据(200 ng、10 ng 和1 ng)或7.15亿数据(0.5 ng和0.1 ng)与人类T2T、lambda和T4参考基因组的复合基因组进行比对。使用Picard计算GC覆盖度,图中显示不同GC含量时(0 – 100%),标准化后覆盖度的分布情况。将人类T2T基因组的GC含量分布绘制为直方图。 结果表明:不同起始量的样本所制备的E5hmC-seq文库皆能获得均一的GC覆盖度。
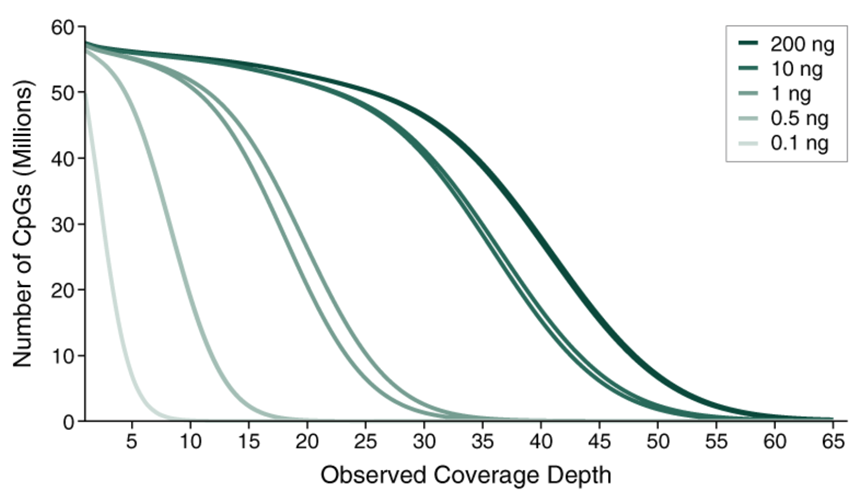
使用Covaris ME220 仪器将0.1 ng至200 ng人脑基因组DNA打断至350 bp,并用作E5hmC-seq的起始样本。构建的文库在Illumina NovaSeq 6000(2x150 bases)上进行测序。使用bwa-meth将每个文库的19亿数据(200 ng、10 ng 和 1 ng)或7.15亿数据(0.5 ng 和 0.1 ng)与人类T2T、lambda 和T4参考基因组的复合基因组进行比对。使用MmethylDackel从比对结果中提取甲基化信息,以methylkit形式提供报告。使用CpG结果,针对所有起始量的E5hmC-seq文库生成CpG图谱。正义链和反义链上的CpG独立计算,在T2T基因组中分析出多达6780万个可能的CpG位点。 使用0.5 ng至200 ng的起始样本时,E5hmC-seq始终可以覆盖超过 5600万个CpG位点;即使使用0.1 ng起始样本时,也可覆盖约4800 万个位点。
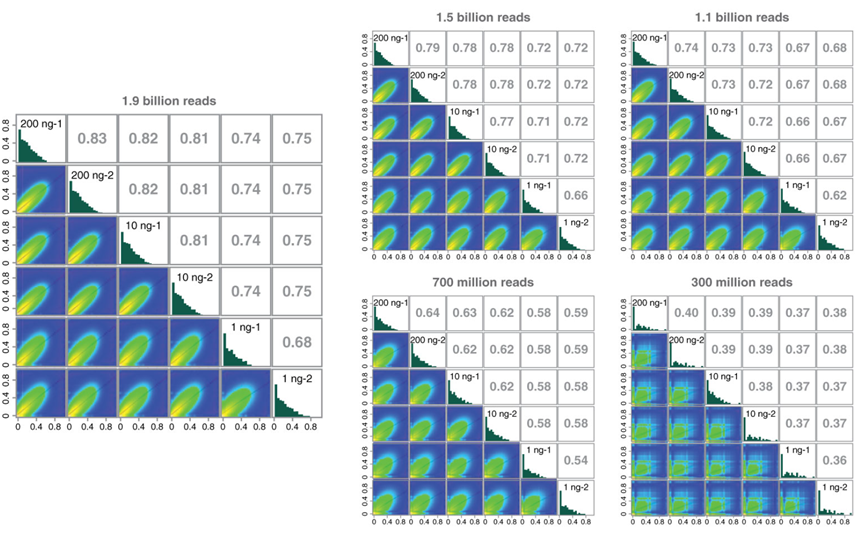
采用methyKit绘制1 ng、10 ng和200 ng起始量下E5hmC-seq文库之间的相关性,19亿数据测序深度,150-base reads,最小覆盖度为1X(所有文库均使用 5,650万个CpG位点)。200 ng和10 ng起始量文库的相关性≥0.81。200 ng和10 ng起始量文库的相关性≥0.81。将200 ng、10 ng和1 ng的E5hmC-seq文库逐步向下采样至约15亿、11亿、7亿和3亿的总reads,并进行相关性分析。我们观察到,与11亿、15亿和19亿reads相关性相比,3亿和7亿reads的相关性较低。 结果表明:由于样本中5hmC信号的丰度较低,因此需要对E5hmC-seq文库进行深度测序。

在科学研究的赛道上,速度与效率是竞争力的代名词。除了这款最新推出的NEBNext®酶学转化法5hmC甲基化建库试剂盒外,不要忘记NEB的明星产品——
NEBNext UltraExpressTM 系列试剂盒!

ta能够大幅提升DNA和RNA文库制备的速度,DNA文库制备:<2小时,起始量范围广:DNA:10-200 ng(机械打断),更在保证高质量的前提下,简化实验流程,减少耗材的使用。

基因有限公司作为NEB全国一级代理,为您提供专业的产品服务!
欢迎扫码添加产品专员, 了解更多产品信息!
